XCellAligner:不可配准病理切片的跨模态细胞对齐(CVPR Findings)
764 字
4 分钟
XCellAligner:不可配准病理切片的跨模态细胞对齐(CVPR Findings)
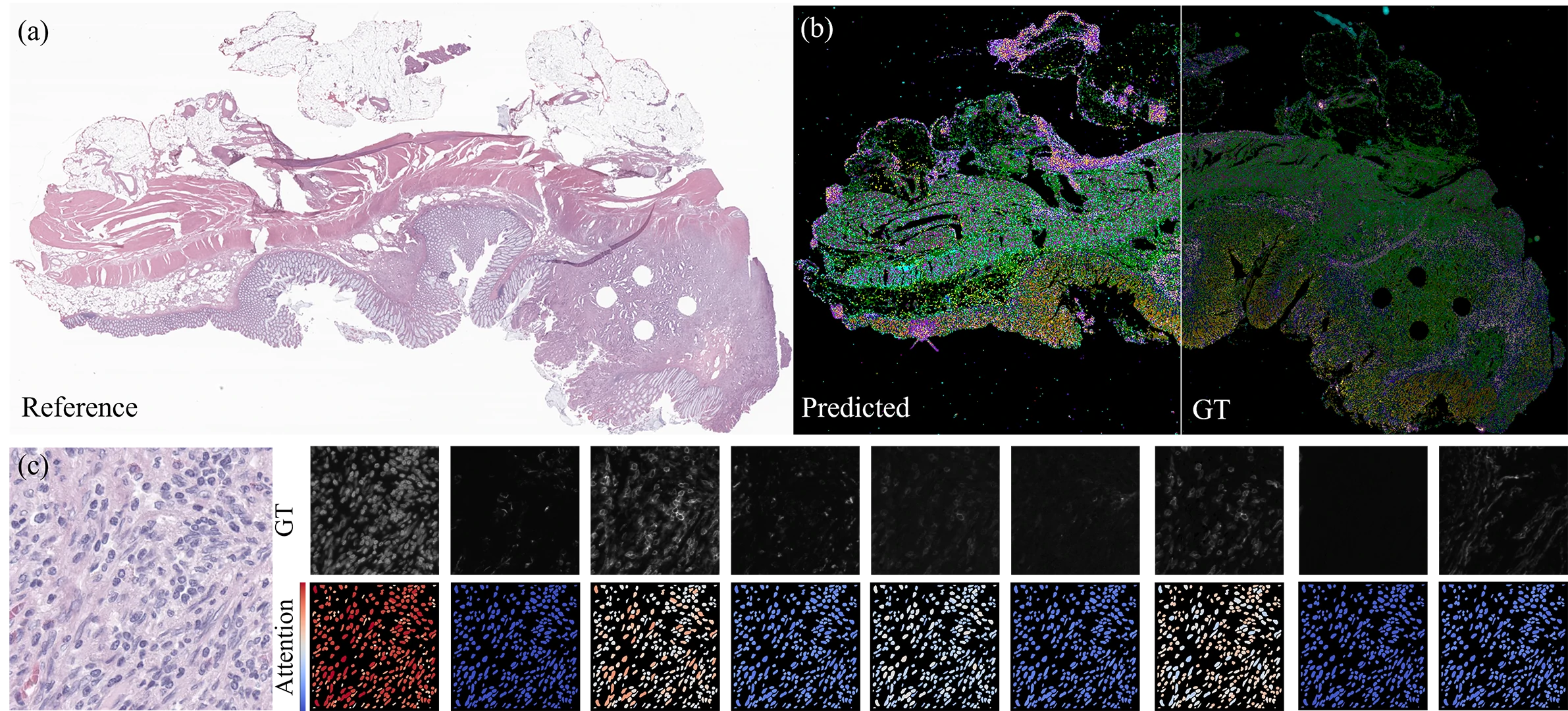
问题定义
在数字病理场景中,H&E 与 mIF 常来自相邻组织切片,天然不存在像素级细胞对应。传统图像配准即便能对齐组织结构,也无法保证细胞语义一一匹配。
我们希望做到:不依赖人工逐细胞标注、不依赖严格像素配准,也能完成跨模态细胞级对齐。
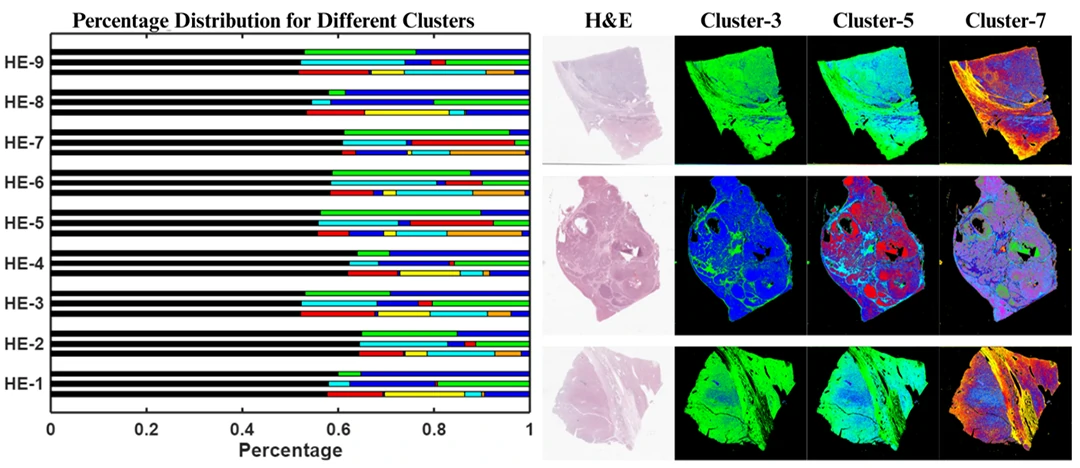
我的工作内容
- 跑通细胞/病灶分割全流程实验与评测
- 参与跨模态语义对齐算法设计与实验验证
- 搭建批量推理、可视化质控与结果导出链路
- 在多数据集上完成消融与泛化评测,支撑临床侧快速验证
核心方法(简化讲法)
整体框架先做模态桥接,再做细胞级精配准。
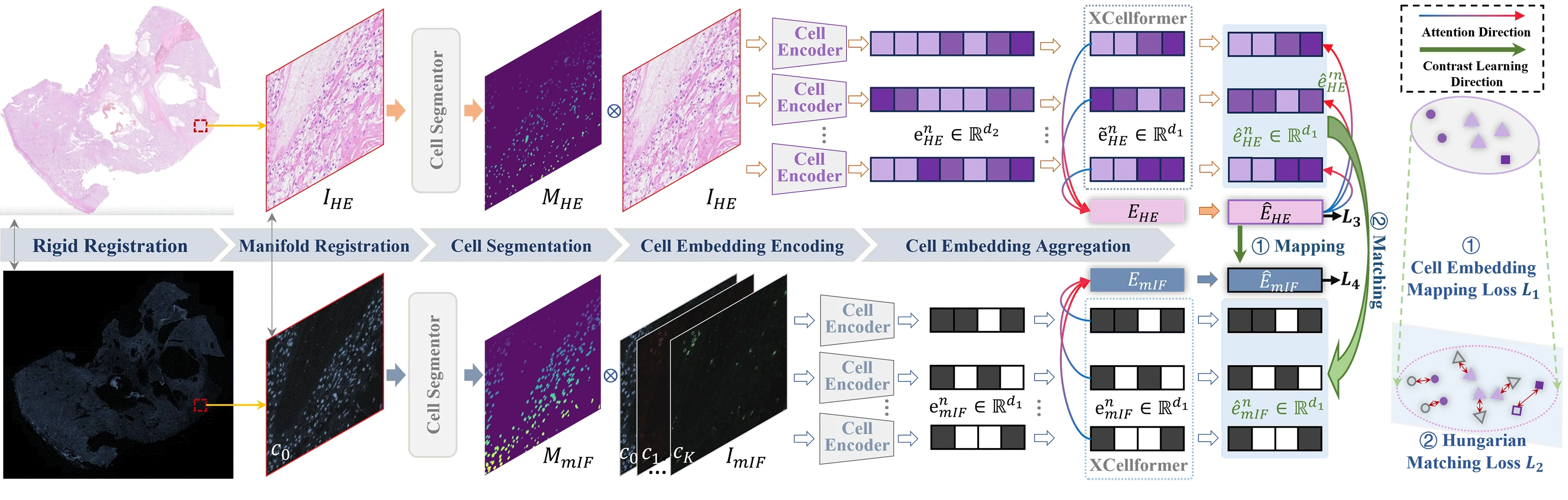
1)模态桥接(patch 级)
将 H&E 与 mIF 的细胞表征映射到共享空间,先完成粗粒度语义对齐。
2)细胞级匹配(Hungarian)
在共享空间里使用匈牙利匹配等策略,进行细粒度 cell-to-cell 对齐。
3)伪匹配迭代优化
结合形态与空间邻域约束生成伪匹配,迭代提升稳定性和泛化能力。
成果与影响
- 在不可配准条件下实现细胞语义迁移
- 多个数据集上较监督基线取得更优细胞识别效果
- 对未见肿瘤类型和组织部位仍保持较好泛化
- 成果产出:CVPR 2026 Findings 一作论文
最终实验对比显示,方法在多个数据集上都具备最佳的效果。
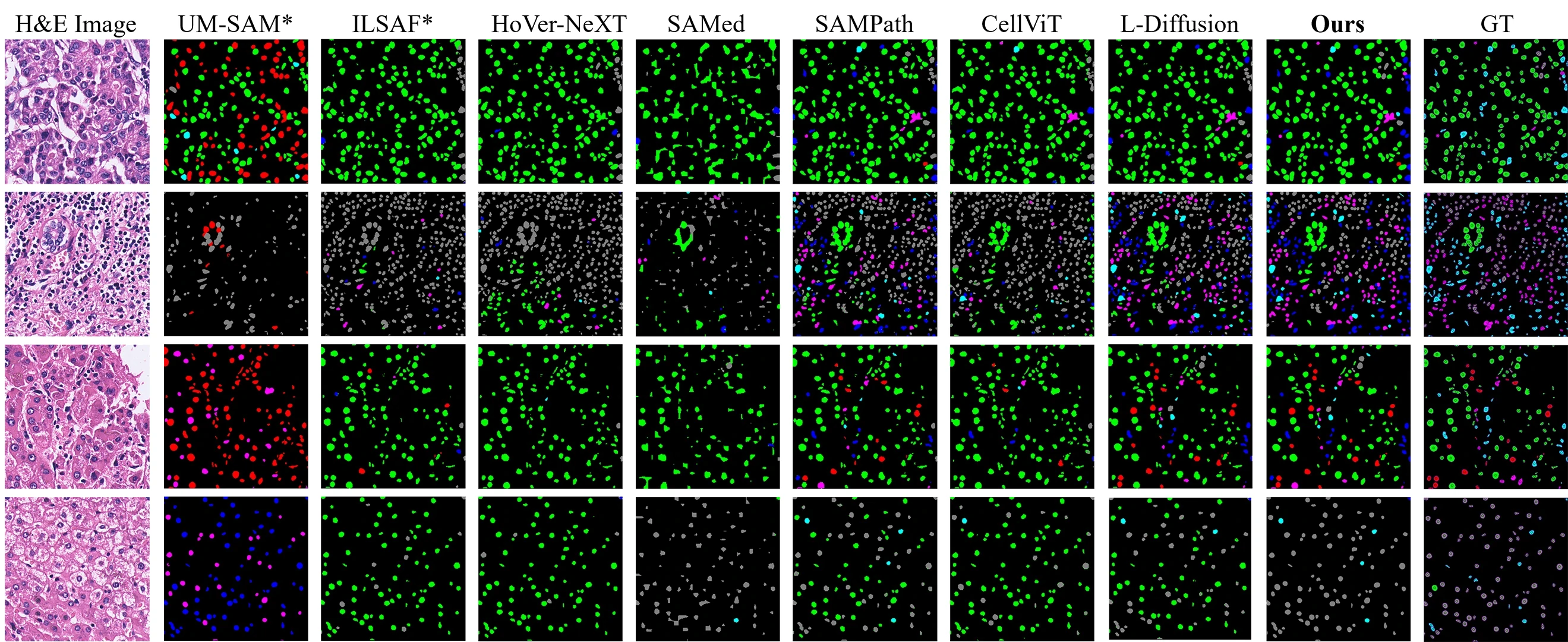
实验结果
为了更系统评估 XCellAligner,这里展示两张关键表格:一张验证“对齐后特征是否泛化到下游任务”,另一张验证“细胞识别是否能在无监督下达到强性能”。
Table 1:对齐后细胞特征(Embedding)性能比较
这组实验将 XCellAligner 与 ResNet-101、CTransPath、UNI2 等特征主干进行对比,并在分类、分割、VQA 三类任务上统一评测(搭配不同解码器)。结果显示,对齐后的特征在多任务指标上更稳定,说明跨模态语义对齐不仅改善单一任务,而是提升了整体可迁移性。
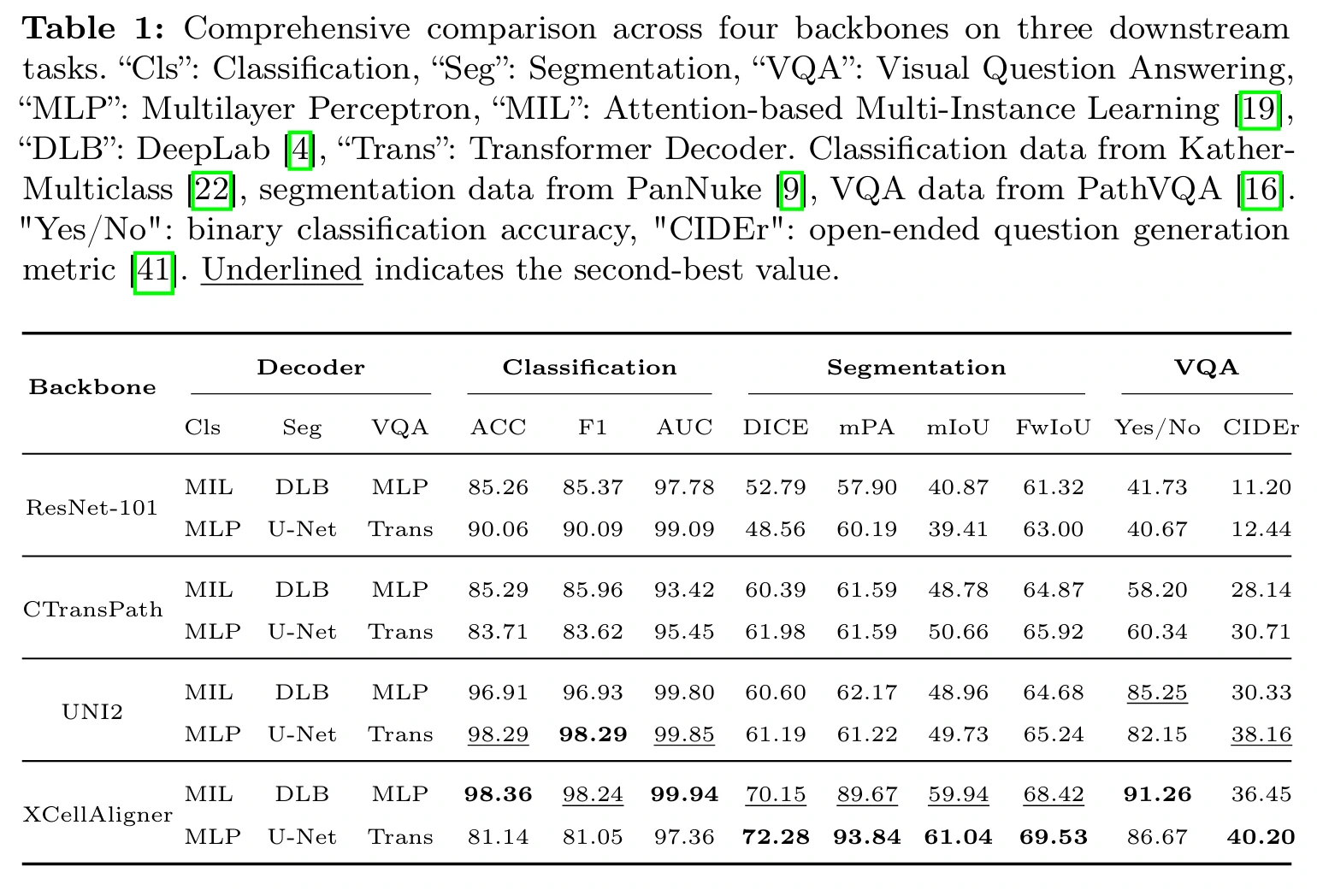
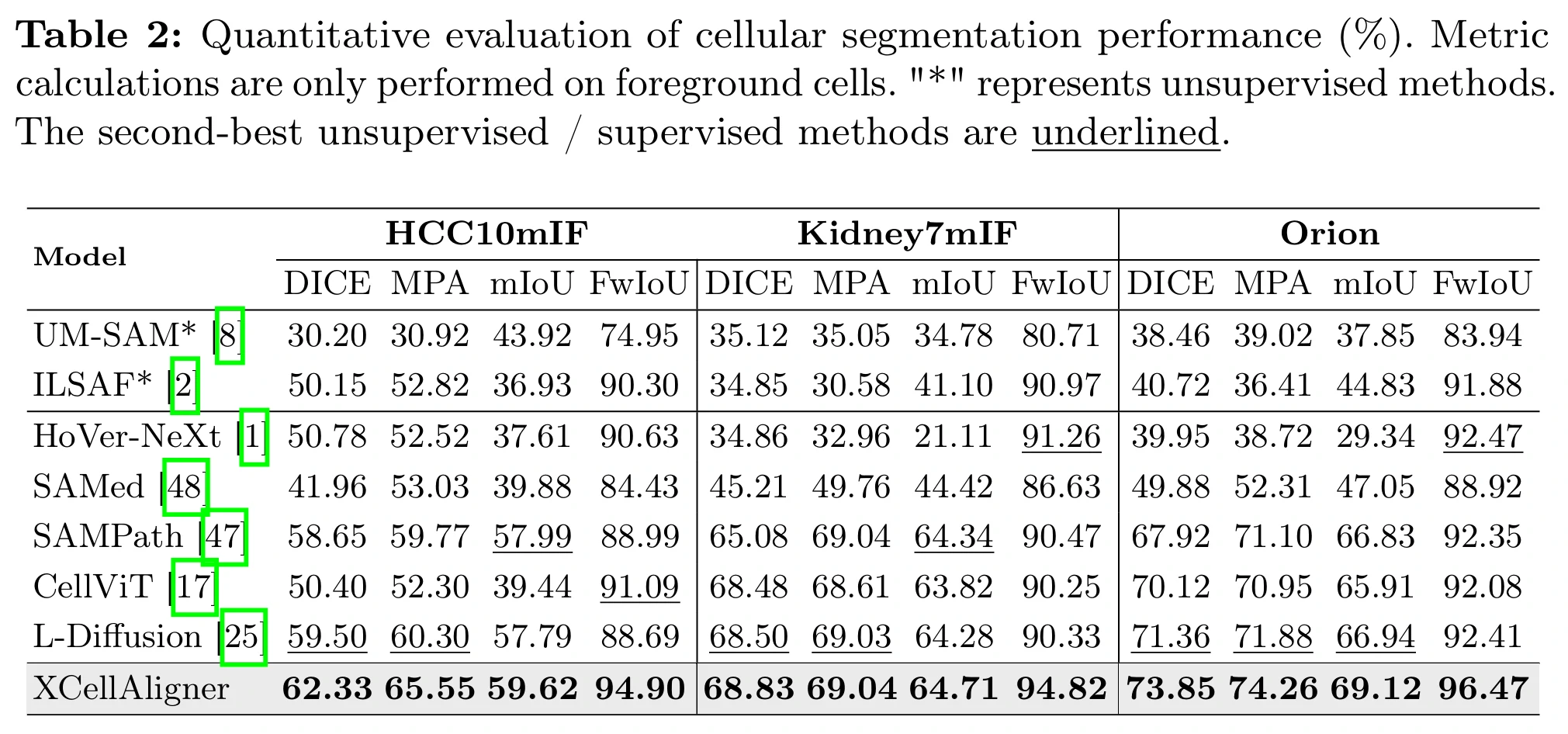
Table 2:细胞识别(语义分割)性能比较
该实验将 XCellAligner 与无监督方法(如 UM-SAM、ILSAF)以及多种全监督 SOTA 方法对比。在 HCC10mIF、Kidney7mIF、Orion 等数据上,XCellAligner 在 DICE、mPA、mIoU、FwIoU 等指标上表现突出,证明我们的无监督对齐特征能和有监督的方法在细胞识别任务上达到甚至超越的水平。
文章分享
如果这篇文章对你有帮助,欢迎分享给更多人!
XCellAligner:不可配准病理切片的跨模态细胞对齐(CVPR Findings)
https://example.com/posts/interview/04-xcellaligner-cvpr/ 最后更新于 2026-01-10,距今已过 78 天
部分内容可能已过时
相关文章 智能推荐
1
D³-RSMDE:40× 加速的遥感单目深度估计(AAAI)
科研项目 在遥感单目深度估计中实现“高保真 + 高效率”,介绍我参与设计的 D³-RSMDE 方法与关键实验结论。
2
REALM-DiT:可控多模态遥感生成(ICML 在投)
实习经历 围绕遥感场景中 RGB、DEM、Land-cover 难以统一生成与对齐的问题,介绍我在滨江研究院科研实习中的核心贡献与成果。
3
RS3DBench:大规模遥感深度估计多模态基准(ECCV 在投)
科研项目 面向遥感深度估计中的几何歧义与数据对齐瓶颈,介绍我参与构建的 RS3DBench 数据集与评测体系。
4
Kaggle MAP:学生数学误区识别竞赛方案复盘
顶尖竞赛 复盘我在 Kaggle MAP(Charting Student Math Misunderstandings)竞赛中获得银牌的核心思路与工程实现。
5
Pinnacle 巅峰对决:面向机考训练的万人级刷题平台
工程项目 介绍我在 Pinnacle 刷题平台中的推荐算法研发与工程实现,重点体现从算法到线上业务的完整闭环。
随机文章 随机推荐














